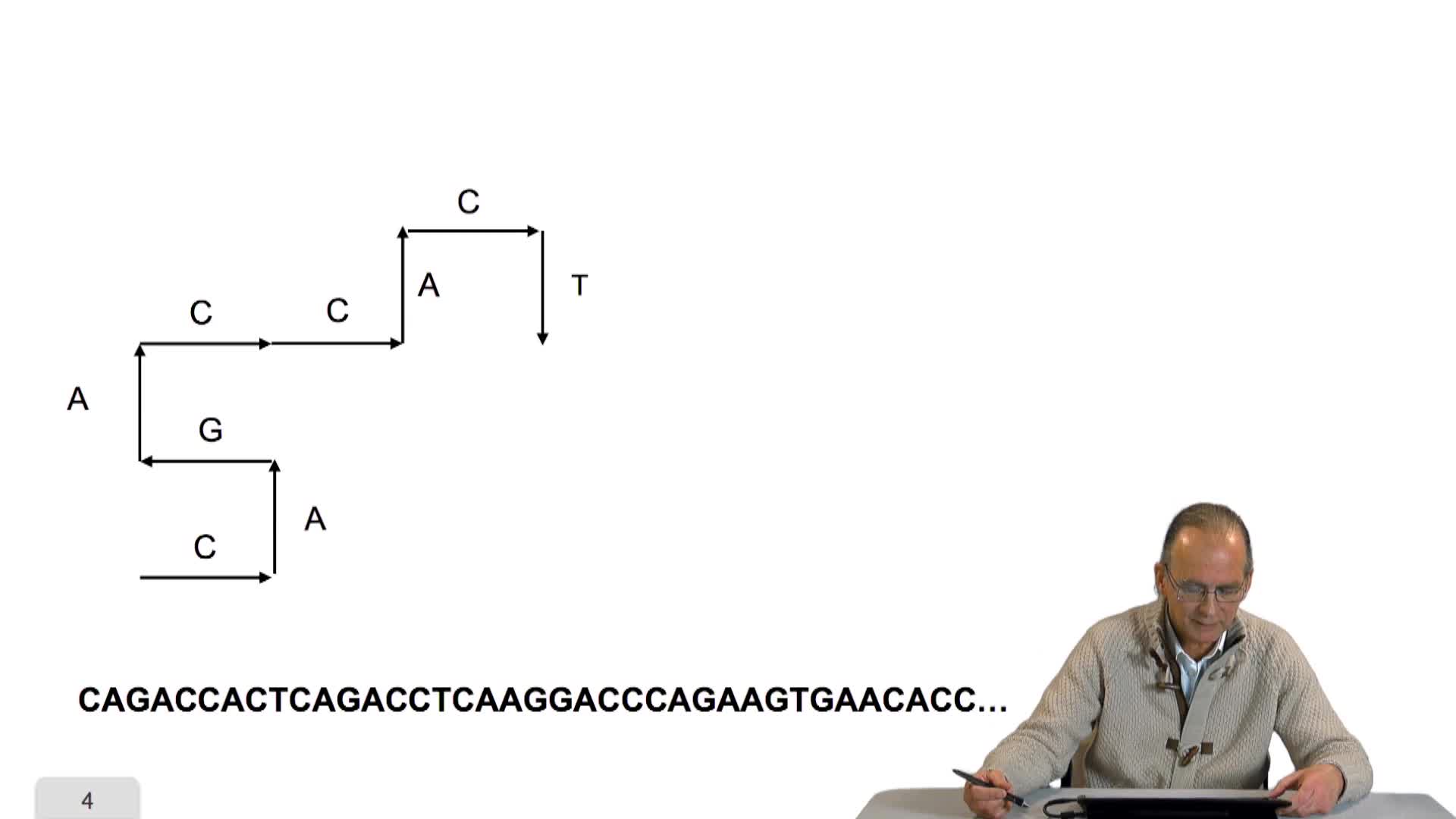Notice
1.1. La cellule, atome du vivant
- document 1 document 2 document 3
- niveau 1 niveau 2 niveau 3
Descriptif
Bienvenue dans cette introduction conjointe aux notions fondamentales de génomique et d'algorithmique, autrement dit, de l'analyse informatique de l'information génétique, ce qu'on peut désigner de façon très synthétique par le terme un domaine scientifique qui est la bio informatique. Au cours de ces 5 parties, nous aborderons des notions fondamentales en commençant par évidemment l'ADN, les séquences génomiques, les textes des génomes, puis de gènes et de protéines et nous nous focaliserons plus particulièrement sur le processus de traduction de gènes en protéines, pour ensuite chercher à concevoir des algorithmes de prédiction de ces gènes dans les textes génomiques, des algorithmes également de comparaison de séquences qui nous permettront de fournir certains éléments sur les fonctions de ces gènes et protéines, et enfin nous verrons comment la connaissance des séquences génomiques d'espèces permet de reconstituer l'arbre d'évolution de ces espèces.
Intervention / Responsable scientifique
Dans la même collection
-
1.5. Compter les nucléotides
RechenmannFrançoisParmentelatThierryNotre premier algorithme vise assez simplement à compter les nucléotides d'une séquence génomique, autrement dit à compter les lettres dans une chaîne de caractères. En entrée, cette chaîne de
-
1.10. Des fenêtres glissantes et recouvrantes
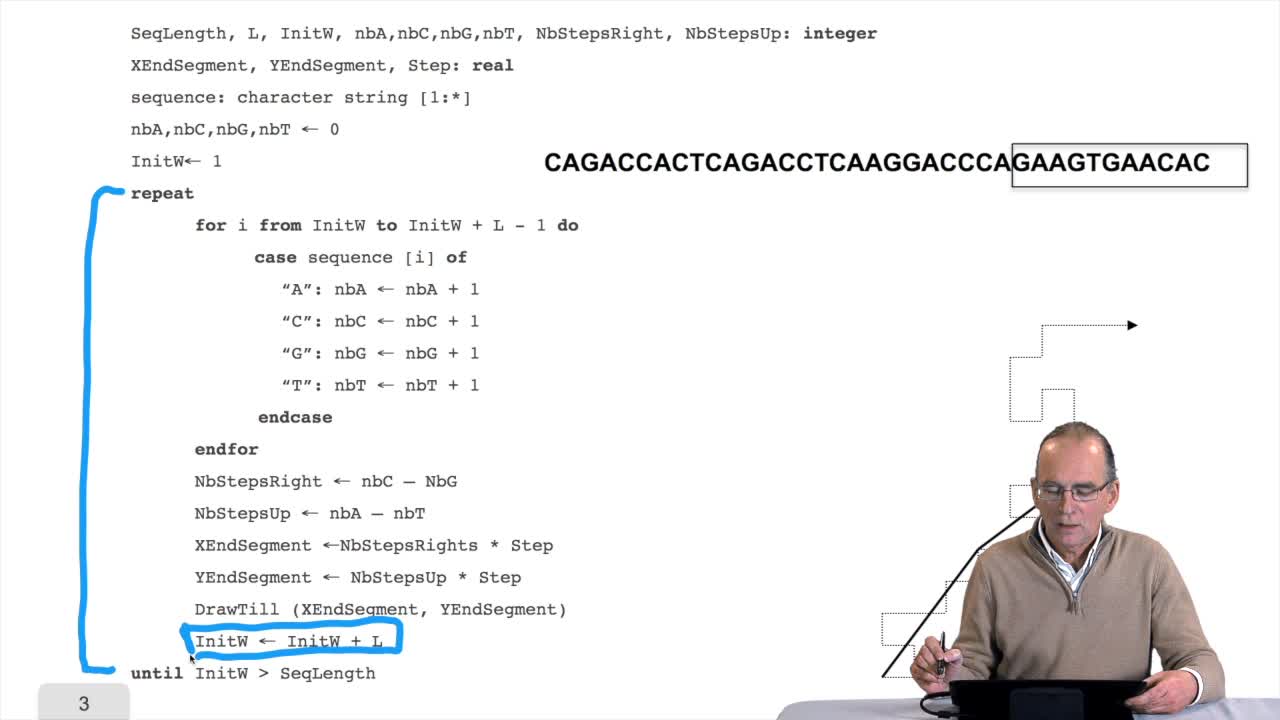
RechenmannFrançoisParmentelatThierryNotre sympathique algorithme de balade sur l'ADN, a permis de mettre en évidence des biais de composition de séquences, a fait apparaître sur le tracé un point de rebroussement que l'on peut
-
1.2. Au cœur de la cellule, la molécule d’ADN
RechenmannFrançoisParmentelatThierryAu cœur de chaque cellule se trouve donc la molécule d'ADN, flottant directement dans le cytoplasme dans le cas des cellules procaryotes, par exemple bactériennes, ou contenue dans le noyau des
-
1.8. Changer l’échelle du chemin
RechenmannFrançoisParmentelatThierryDans la session précédente, je vous ai proposé de m'accompagner dans une balade sur l'ADN. En fait un parcours de la séquence avec un tracé de segments, dont l'orientation dépendait de la lettre
-
1.4. Qu’est-ce qu’un algorithme ?
RechenmannFrançoisParmentelatThierryLes génomes peuvent donc être vus comme une longue suite de lettres écrites dans l'alphabet : A, C, G et T. Comment interpréter ces textes ? Ça va être le sujet de la bio-informatique à l'aide d
-
1.9. Prédire l’origine de réplication
RechenmannFrançoisParmentelatThierryNous avons écrit un algorithme sympathique en ce qu'il dessine un chemin conforme à la succession des lettres d'une séquence génomique. Cet algorithme simple, au-delà du dessin qu'il produit, est-il
-
1.6. Contenu en G-C et A-T des séquences
RechenmannFrançoisParmentelatThierryLes algorithmes qui travaillent sur les séquences génomiques, sur les textes génomiques, doivent produire des résultats interprétables et utiles aux biologistes. Nous allons voir que même sur l
-
1.3. L’ADN code l’information génétique
RechenmannFrançoisParmentelatThierryL'ADN, cette longue molécule, porte l'information génétique. Autrement dit, l'information qui est nécessaire à la cellule pour fonctionner et se reproduire. Regardons de plus près cette information
-
1.7. Promenade sur l’ADN
RechenmannFrançoisParmentelatThierryQuand les biologistes se sont trouvés confrontés au premier texte génomique, dans la deuxième moitié des années 70, ils ont été quelque peu désemparés. On peut le comprendre. Encore une fois, regardez
Avec les mêmes intervenants et intervenantes
-
1.1. The cell, atom of the living world
RechenmannFrançoisWelcome to this introduction to bioinformatics. We will speak of genomes and algorithms. More specifically, we will see how genetic information can be analysed by algorithms. In these five weeks to
-
1.9. Predicting the origin of DNA replication?
RechenmannFrançoisWe have seen a nice algorithm to draw, let's say, a DNA sequence. We will see that first, we have to correct a little bit this algorithm. And then we will see how such as imple algorithm can provide
-
2.8. DNA sequencing
RechenmannFrançoisDuring the last session, I explained several times how it was important to increase the efficiency of sequences processing algorithm because sequences arevery long and there are large volumes of
-
3.5. Making the predictions more reliable
RechenmannFrançoisWe have got a bacterial gene predictor but the way this predictor works is rather crude and if we want to have more reliable results, we have to inject into this algorithmmore biological knowledge. We
-
4.6. A path is optimal if all its sub-paths are optimal
RechenmannFrançoisA sequence alignment between two sequences is a path in a grid. So that, an optimal sequence alignmentis an optimal path in the same grid. We'll see now that a property of this optimal path provides
-
5.1. The tree of life
RechenmannFrançoisWelcome to this fifth and last week of our course on genomes and algorithms that is the computer analysis of genetic information. During this week, we will firstsee what phylogenetic trees are and how
-
1.4. What is an algorithm?
RechenmannFrançoisWe have seen that a genomic textcan be indeed a very long sequence of characters. And to interpret this sequence of characters, we will need to use computers. Using computers means writing program.
-
2.2. Genes: from Mendel to molecular biology
RechenmannFrançoisThe notion of gene emerged withthe works of Gregor Mendel. Mendel studied the inheritance on some traits like the shape of pea plant seeds,through generations. He stated the famous laws of inheritance
-
2.10. How to find genes?
RechenmannFrançoisGetting the sequence of the genome is only the beginning, as I explained, once you have the sequence what you want to do is to locate the gene, to predict the function of the gene and maybe study the
-
3.8. Probabilistic methods
RechenmannFrançoisUp to now, to predict our gene,we only rely on the process of searching certain strings or patterns. In order to further improve our gene predictor, the idea is to use, to rely onprobabilistic methods
-
4.3. Measuring sequence similarity
RechenmannFrançoisSo we understand why gene orprotein sequences may be similar. It's because they evolve togetherwith the species and they evolve in time, there aremodifications in the sequence and that the sequence
-
5.3. Building an array of distances
RechenmannFrançoisSo using the sequences of homologous gene between several species, our aim is to reconstruct phylogenetic tree of the corresponding species. For this, we have to comparesequences and compute distances
Sur le même thème
-
La voix, une donnée identifiante à protéger
VincentEmmanuelEmmanuel Vincent, chercheur au Centre Inria de l'Université de Lorraine et au Loria (Laboratoire lorrain de recherche en informatique et ses applications), présente sa recherche sur l'anonymisation de
-
Podcast 1/4 d'heure avec : Emmanuel Vincent, chercheur au Centre Inria de l'Université de Lorraine …
VincentEmmanuelRencontre avec Emmanuel Vincent - chercheur au Centre Inria de l'Université de Lorraine et Loria (Laboratoire lorrain de recherche en informatique et ses applications).
-
Stockage de données numériques sur ADN synthétique : Introduction au domaine
AntoniniMarcDuprazElsaLavenierDominiquePrésentation globale des différentes étapes du stockage de données sur des molécules d'ADN synthétique
-
Stockage de données numériques sur ADN synthétique : Production des données: synthèse, séquençage
LavenierDominiqueBarbryPascalDescription des opérations d'écriture et de lecture des molécules d'ADN : synthèse et séquençage.
-
Stockage de données numériques sur ADN synthétique : Reconstruction des données
LavenierDominiqueTraitement des données après séquençage
-
Stockage de données numériques sur ADN synthétique : Codage Canal
DuprazElsaTechniques de codage pour le stockage de données sur ADN
-
Stockage de données numériques sur ADN synthétique : Codage Source
AntoniniMarcCodage source pour le stockage de données sur ADN synthétique
-
Stockage de données numériques sur ADN synthétique : Théorie de l'information
Kas HannaSergeQuelle quantité d'information peut-on stocker et récupérer de manière fiable dans l'ADN ?
-
The tree of life
AbbySophieLes Rencontres Exobiologiques pour Doctorants (RED) sont une école de formation sur les « bases de l'astrobiologie ». L’édition 2025 s’est tenue du 16 au 21 mars au Parc Ornithologique du Teich.
-
Machines algorithmiques, mythes et réalités
MazenodVincentVincent Mazenod, informaticien, partage le fruit de ses réflexions sur l'évolution des outils numériques, en lien avec les problématiques de souveraineté, de sécurité et de vie privée...
-
Désassemblons le numérique - #Episode11 : Les algorithmes façonnent-ils notre société ?
SchwartzArnaudLima PillaLaércioEstériePierreSalletFrédéricFerbosAudeRoumanosRayyaChraibi KadoudIkramUn an après le tout premier hackathon sur les méthodologies d'enquêtes journalistiques sur les algorithmes, ce nouvel épisode part à la rencontre de différents points de vue sur les algorithmes.
-
Les machines à enseigner. Du livre à l'IA...
BruillardÉricQue peut-on, que doit-on déléguer à des machines ? C'est l'une des questions explorées par Éric Bruillard qui, du livre aux IA génératives, expose l'évolution des machines à enseigner...