Notice
3.5. Comment améliorer la qualité des prédictions ?
- document 1 document 2 document 3
- niveau 1 niveau 2 niveau 3
Descriptif
Il faut toujours le répéter et le souligner, les algorithmes qui déterminent des gènes déterminent des gènes candidats. Ce sont des prédictions de gènes. Donc la question est de savoir s'il est éventuellement possible d'améliorer nos algorithmes de façon à améliorer la qualité de nos prédictions. Nous allons voir qu'il y a en restant dans la même logique de notre algorithme précédent, effectivement la possibilité d'améliorer la qualité, la prédiction de régions codantes sur un brin d'ADN.
Pour ce faire, il nous faut introduire une notion de biologie moléculaire importante qui est le ribosome. De quoi s'agit-il ? Vous avez ici le schéma d'une partie d'une cellule que vous voyez immédiatement être une cellule eucaryote, puisque il existe un noyau. L'ADN est transcrit dans un brin d'ARN messager qui quitte le noyau. Une fois, qu'il est au sein du cytoplasme, il intéresse le ribosome qui est une véritable tête de lecture de l'ARN messager. L'ARN va passer devant cette tête de lecture. Et la traduction va avoir lieu par un mécanisme que je ne détaille pas ici, mais qui réussit à mettre en correspondance pour chaque codon de la région codante, l'acide aminé correspondant pour construire la chaîne d'acide aminé qui est la protéine...
Intervention / Responsable scientifique
Thème
Documentation
Dans la même collection
-
3.7. Index et arbre des suffixes
RechenmannFrançoisParmentelatThierryIl y a donc deux approches pour améliorer la performance des algorithmes de recherche d'un motif dans une chaîne de caractères. La première approche consiste à pré-traiter le motif. On a vu un exemple
-
3.1. Tous les gènes se terminent sur un codon stop
RechenmannFrançoisParmentelatThierryUne fois la séquence d'un génome complet obtenue, débute la phase d'annotation. L'annotation elle-même consiste tout d'abord à rechercher la localisation, c'est-à-dire la position des gènes sur cette
-
3.10. La prédiction de gènes dans les génomes eucaryotes
RechenmannFrançoisParmentelatThierrySi nous disposons actuellement de prédicteurs de gènes dans les génomes procaryotes de très bonne efficacité, avec des prédictions relativement fiables, c'est en fait loin d'être le cas sur les
-
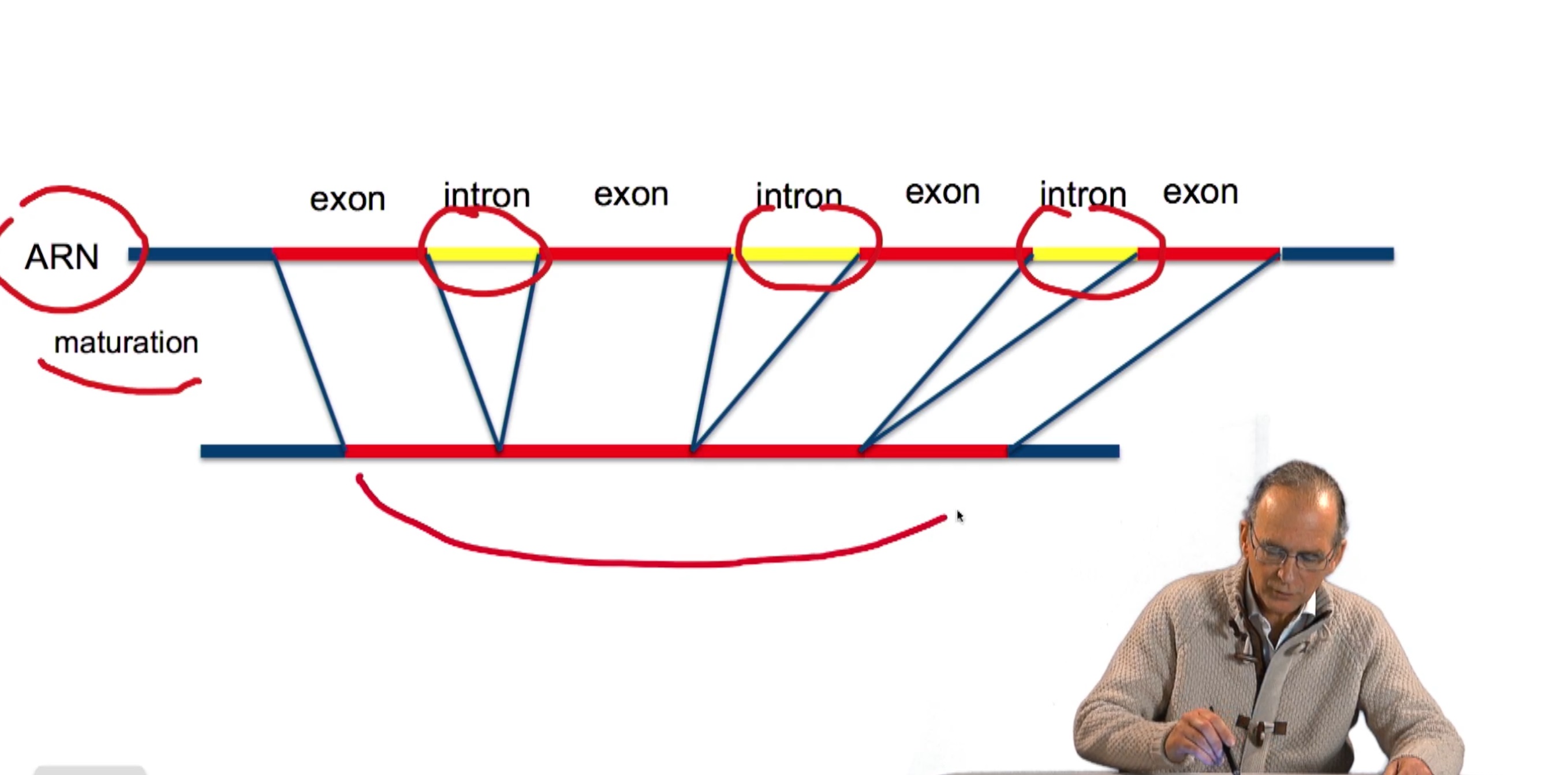
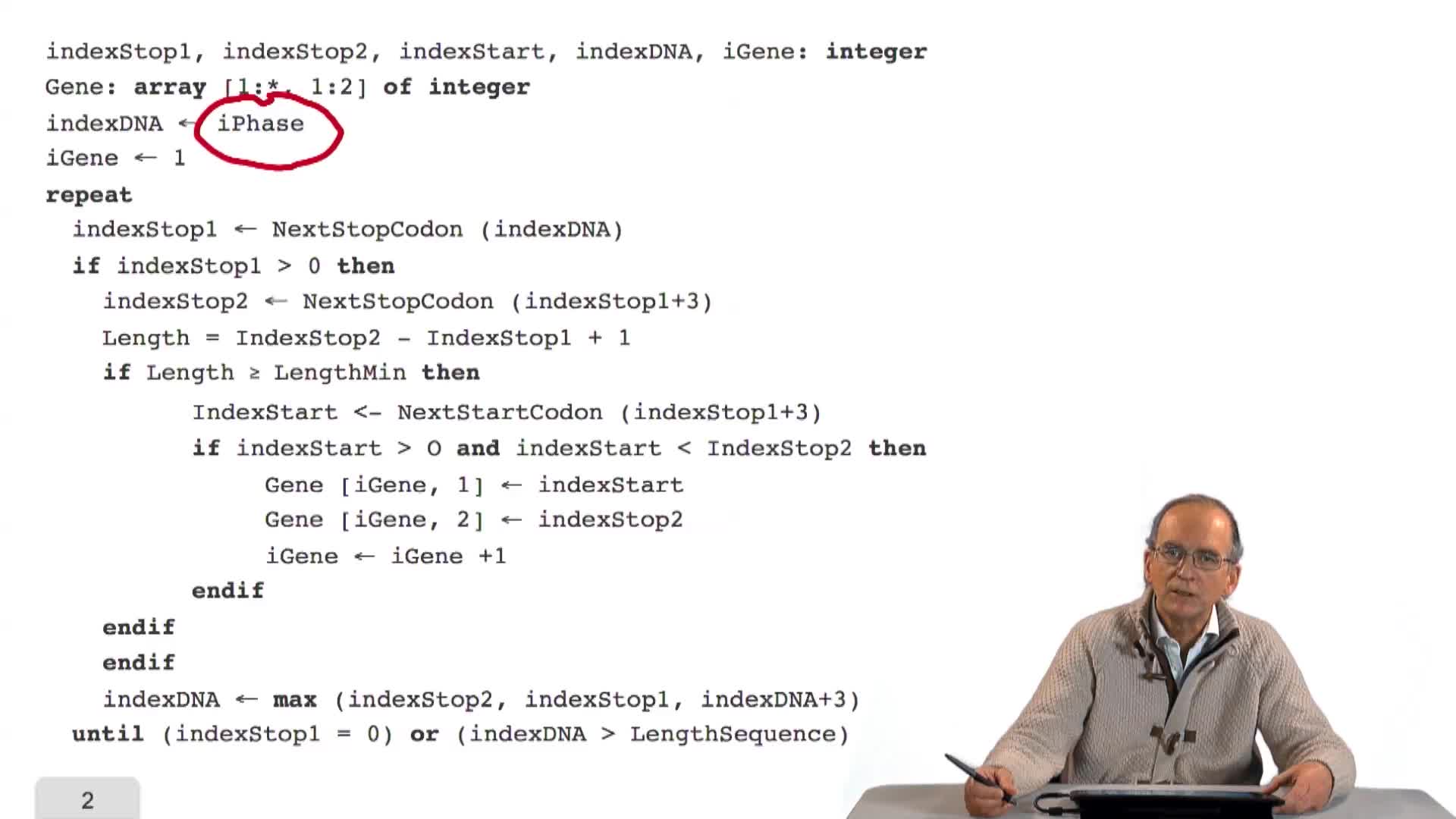
3.4. Prédiction de tous les gènes d’une séquence
RechenmannFrançoisParmentelatThierryEn combinant de façon adéquate la recherche des triplés Stop et Start sur un brin d'ADN, nous avons obtenu un algorithme qui prédit les gènes sur ce brin, mais également sur une phase. C'est-à-dire en
-
3.8. Des méthodes probabilistes à la rescousse
RechenmannFrançoisParmentelatThierryNous avons vu comment la qualité des prédictions de gènes dans un génome bactérien, pouvait être améliorée à travers la recherche d'occurrences de motifs particuliers liés au site de fixation du
-
3.2. Un algorithme simple de prédiction de gènes
RechenmannFrançoisParmentelatThierrySur la base des principes énoncés précédemment, nous allons écrire un premier algorithme de prédiction de gènes sur un texte génomique procaryote. Je rappelle ces principes. L'idée est la suivante :
-
3.6. L’algorithme de Boyer-Moore
RechenmannFrançoisParmentelatThierryVous avez compris que la recherche de motifs, c'est-à-dire de sous-chaînes de caractères dans une chaîne plus importante, était un composant important de beaucoup d'algorithmes de bio-informatique.
-
3.9. Comment évaluer la qualité de prédiction des méthodes ?
RechenmannFrançoisParmentelatThierryNous avons vu qu'il était possible, ou du moins nous le pensions, améliorer la qualité de prédiction des gènes sur un génome bactérien en introduisant des démarches supplémentaires, de recherches de
-
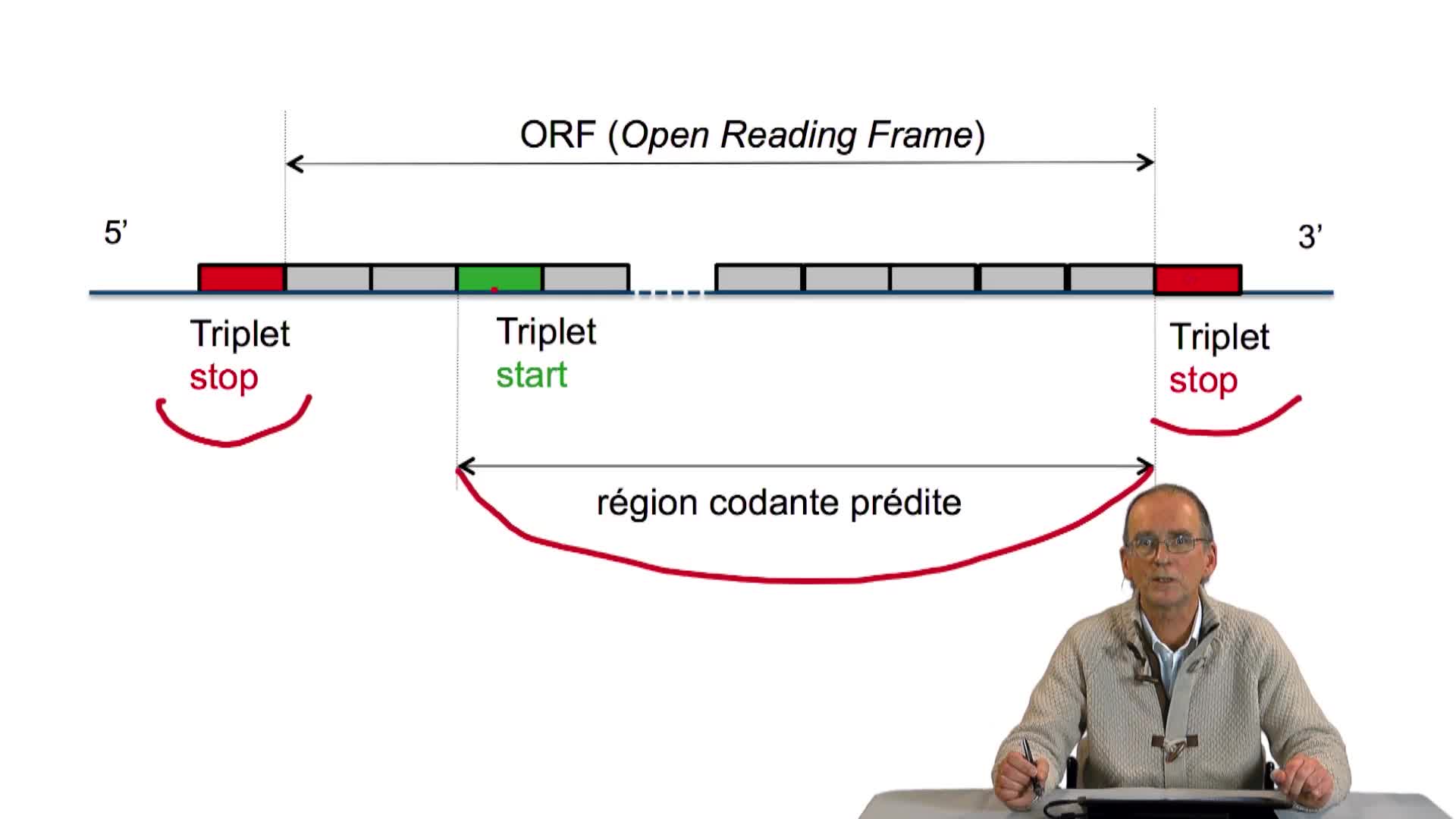
3.3. À la recherche des codons start et stop
RechenmannFrançoisParmentelatThierryNous avons écrit la structure, l'ossature d'un algorithme de prédiction de gènes dans un génome bactérien, en utilisant les principes que nous avions énoncés précédemment. Cet algorithme est incomplet
Avec les mêmes intervenants et intervenantes
-
1.4. What is an algorithm?
RechenmannFrançoisWe have seen that a genomic textcan be indeed a very long sequence of characters. And to interpret this sequence of characters, we will need to use computers. Using computers means writing program.
-
2.2. Genes: from Mendel to molecular biology
RechenmannFrançoisThe notion of gene emerged withthe works of Gregor Mendel. Mendel studied the inheritance on some traits like the shape of pea plant seeds,through generations. He stated the famous laws of inheritance
-
2.10. How to find genes?
RechenmannFrançoisGetting the sequence of the genome is only the beginning, as I explained, once you have the sequence what you want to do is to locate the gene, to predict the function of the gene and maybe study the
-
3.8. Probabilistic methods
RechenmannFrançoisUp to now, to predict our gene,we only rely on the process of searching certain strings or patterns. In order to further improve our gene predictor, the idea is to use, to rely onprobabilistic methods
-
4.3. Measuring sequence similarity
RechenmannFrançoisSo we understand why gene orprotein sequences may be similar. It's because they evolve togetherwith the species and they evolve in time, there aremodifications in the sequence and that the sequence
-
5.3. Building an array of distances
RechenmannFrançoisSo using the sequences of homologous gene between several species, our aim is to reconstruct phylogenetic tree of the corresponding species. For this, we have to comparesequences and compute distances
-
1.7. DNA walk
RechenmannFrançoisWe will now design a more graphical algorithm which is called "the DNA walk". We shall see what does it mean "DNA walk". Walk on to DNA. Something like that, yes. But first, just have a look again at
-
2.6. Algorithms + data structures = programs
RechenmannFrançoisBy writing the Lookup GeneticCode Function, we completed our translation algorithm. So we may ask the question about the algorithm, does it terminate? Andthe answer is yes, obviously. Is it pertinent,
-
3.3. Searching for start and stop codons
RechenmannFrançoisWe have written an algorithm for finding genes. But you remember that we arestill to write the two functions for finding the next stop codonand the next start codon. Let's see how we can do that. We
-
4.1. How to predict gene/protein functions?
RechenmannFrançoisLast week we have seen that annotating a genome means first locating the genes on the DNA sequences that is the genes, the region coding for proteins. But this is indeed the first step,the next very
-
4.10. How efficient is this algorithm?
RechenmannFrançoisWe have seen the principle of an iterative algorithm in two paths for aligning and comparing two sequences of characters, here DNA sequences. And we understoodwhy the iterative version is much more
-
5.7. The application domains in microbiology
RechenmannFrançoisBioinformatics relies on many domains of mathematics and computer science. Of course, algorithms themselves on character strings are important in bioinformatics, we have seen them. Algorithms and
Sur le même thème
-
La voix, une donnée identifiante à protéger
VincentEmmanuelEmmanuel Vincent, chercheur au Centre Inria de l'Université de Lorraine et au Loria (Laboratoire lorrain de recherche en informatique et ses applications), présente sa recherche sur l'anonymisation de
-
Podcast 1/4 d'heure avec : Emmanuel Vincent, chercheur au Centre Inria de l'Université de Lorraine …
VincentEmmanuelRencontre avec Emmanuel Vincent - chercheur au Centre Inria de l'Université de Lorraine et Loria (Laboratoire lorrain de recherche en informatique et ses applications).
-
Stockage de données numériques sur ADN synthétique : Introduction au domaine
AntoniniMarcDuprazElsaLavenierDominiquePrésentation globale des différentes étapes du stockage de données sur des molécules d'ADN synthétique
-
Stockage de données numériques sur ADN synthétique : Production des données: synthèse, séquençage
LavenierDominiqueBarbryPascalDescription des opérations d'écriture et de lecture des molécules d'ADN : synthèse et séquençage.
-
Stockage de données numériques sur ADN synthétique : Reconstruction des données
LavenierDominiqueTraitement des données après séquençage
-
Stockage de données numériques sur ADN synthétique : Codage Canal
DuprazElsaTechniques de codage pour le stockage de données sur ADN
-
Stockage de données numériques sur ADN synthétique : Codage Source
AntoniniMarcCodage source pour le stockage de données sur ADN synthétique
-
Stockage de données numériques sur ADN synthétique : Théorie de l'information
Kas HannaSergeQuelle quantité d'information peut-on stocker et récupérer de manière fiable dans l'ADN ?
-
The tree of life
AbbySophieLes Rencontres Exobiologiques pour Doctorants (RED) sont une école de formation sur les « bases de l'astrobiologie ». L’édition 2025 s’est tenue du 16 au 21 mars au Parc Ornithologique du Teich.
-
Machines algorithmiques, mythes et réalités
MazenodVincentVincent Mazenod, informaticien, partage le fruit de ses réflexions sur l'évolution des outils numériques, en lien avec les problématiques de souveraineté, de sécurité et de vie privée...
-
Désassemblons le numérique - #Episode11 : Les algorithmes façonnent-ils notre société ?
SchwartzArnaudLima PillaLaércioEstériePierreSalletFrédéricFerbosAudeRoumanosRayyaChraibi KadoudIkramUn an après le tout premier hackathon sur les méthodologies d'enquêtes journalistiques sur les algorithmes, ce nouvel épisode part à la rencontre de différents points de vue sur les algorithmes.
-
Les machines à enseigner. Du livre à l'IA...
BruillardÉricQue peut-on, que doit-on déléguer à des machines ? C'est l'une des questions explorées par Éric Bruillard qui, du livre aux IA génératives, expose l'évolution des machines à enseigner...