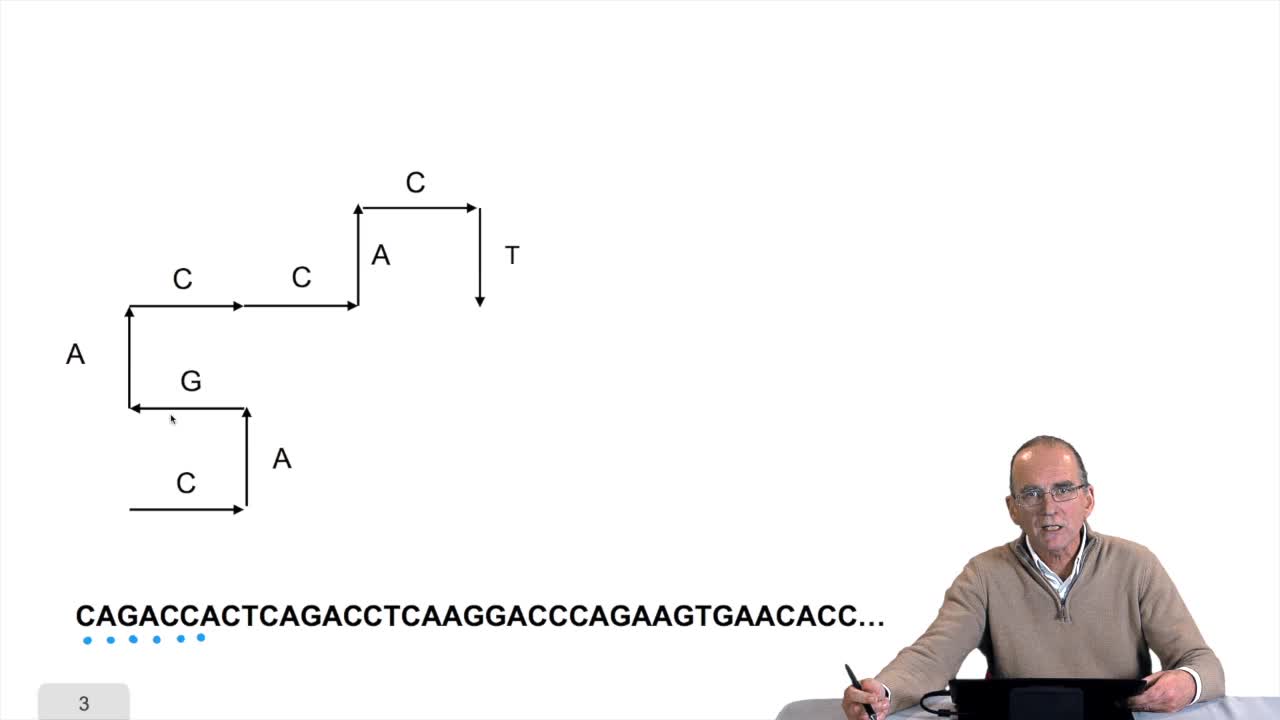Notice
Bio-informatique et applications
- document 1 document 2 document 3
- niveau 1 niveau 2 niveau 3
Descriptif
La séquence de caractères est un des objets que lesinformaticiens connaissent bien et pour lequel ils ont développé de trèsnombreux algorithmes. C’est donc très naturellement que l’informatique et lessciences du vivant se sont rencontrées autour de la problématique de l’analysedes séquences génomiques.
Thème
Avec les mêmes intervenants et intervenantes
-
1.8. Compressing the DNA walk
RECHENMANN François
We have written the algorithm for the circle DNA walk. Just a precision here: the kind of drawing we get has nothing to do with the physical drawing of the DNA molecule. It is a symbolic
-
2.7. The algorithm design trade-off
RECHENMANN François
We saw how to increase the efficiencyof our algorithm through the introduction of a data structure. Now let's see if we can do even better. We had a table of index and weexplain how the use of these
-
3.4. Predicting all the genes in a sequence
RECHENMANN François
We have written an algorithm whichis able to locate potential genes on a sequence but only on one phase because we are looking triplets after triplets. Now remember that the genes maybe located on
-
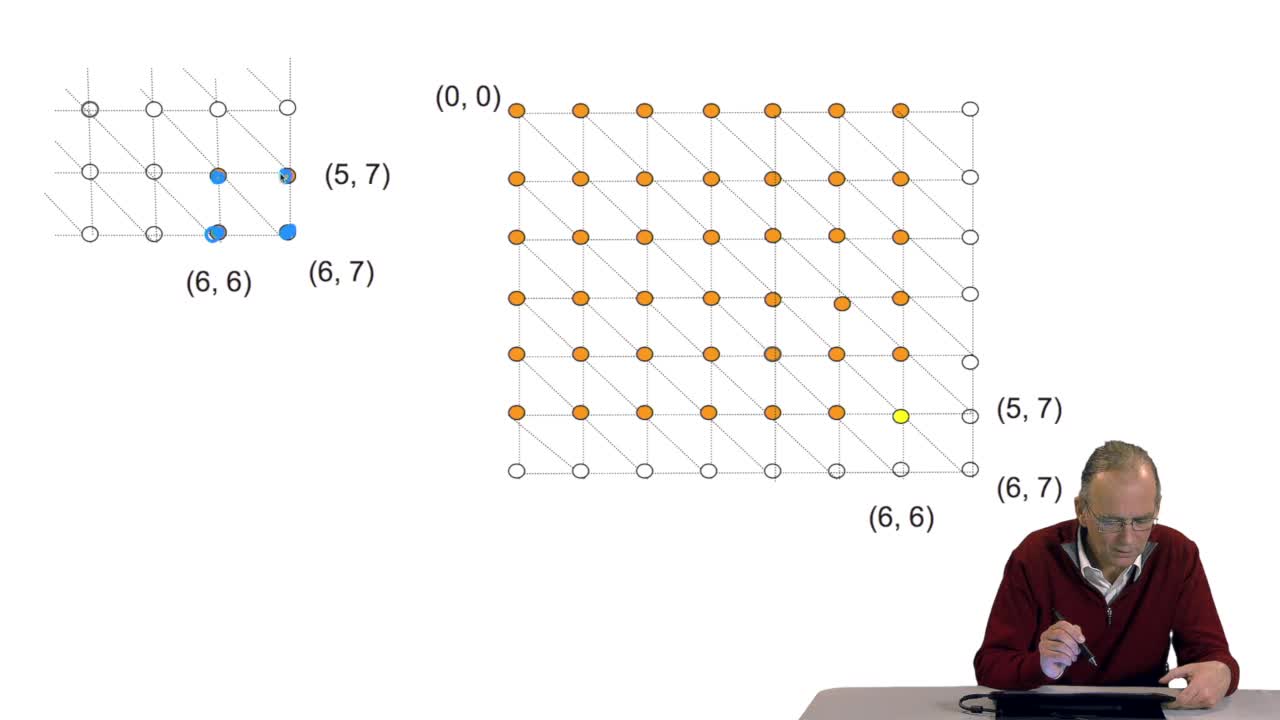
4.7. Alignment costs
RECHENMANN François
We have seen how we can compute the cost of the path ending on the last node of our grid if we know the cost of the sub-path ending on the three adjacent nodes. It is time now to see more deeply why
-
4.9. Recursion can be avoided: an iterative version
RECHENMANN François
We have written a recursive function to compute the optimal path that is an optimal alignment between two sequences. Here all the examples I gave were onDNA sequences, four letter alphabet. OK. The
-
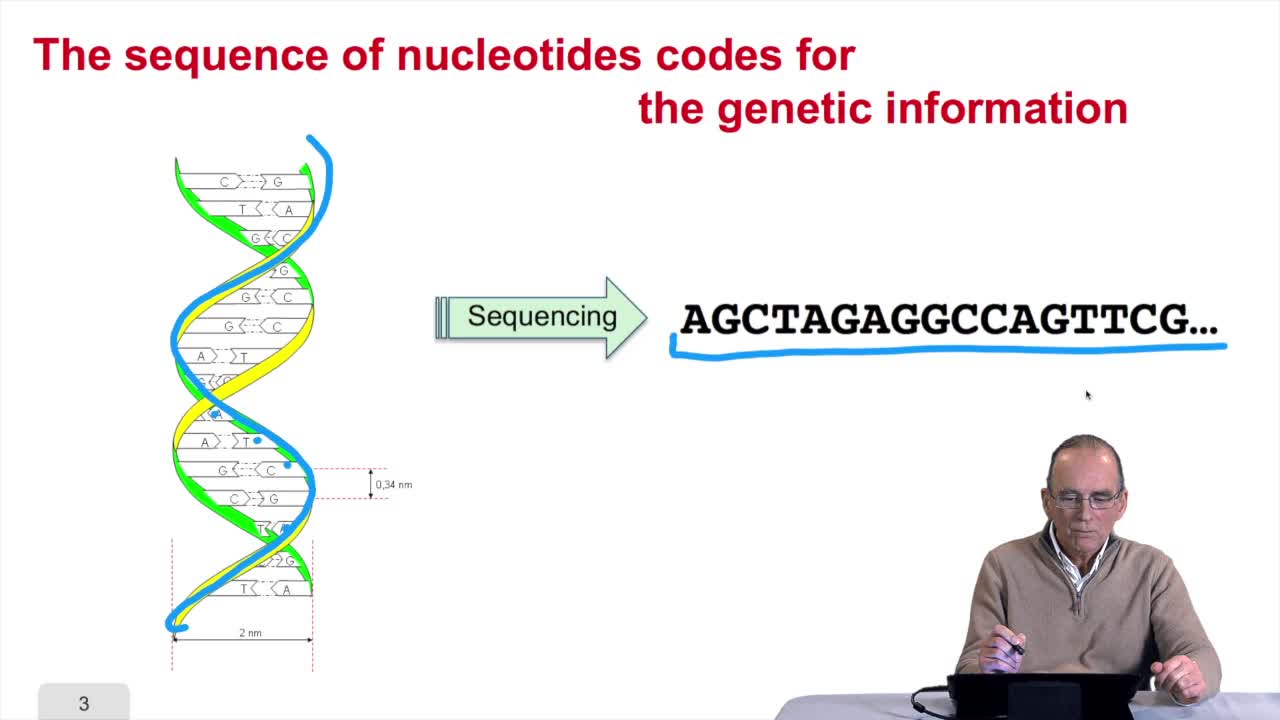
1.3. DNA codes for genetic information
RECHENMANN François
Remember at the heart of any cell,there is this very long molecule which is called a macromolecule for this reason, which is the DNA molecule. Now we will see that DNA molecules support what is called
-
2.1. The sequence as a model of DNA
RECHENMANN François
Welcome back to our course on genomes and algorithms that is a computer analysis ofgenetic information. Last week we introduced the very basic concept in biology that is cell, DNA, genome, genes
-
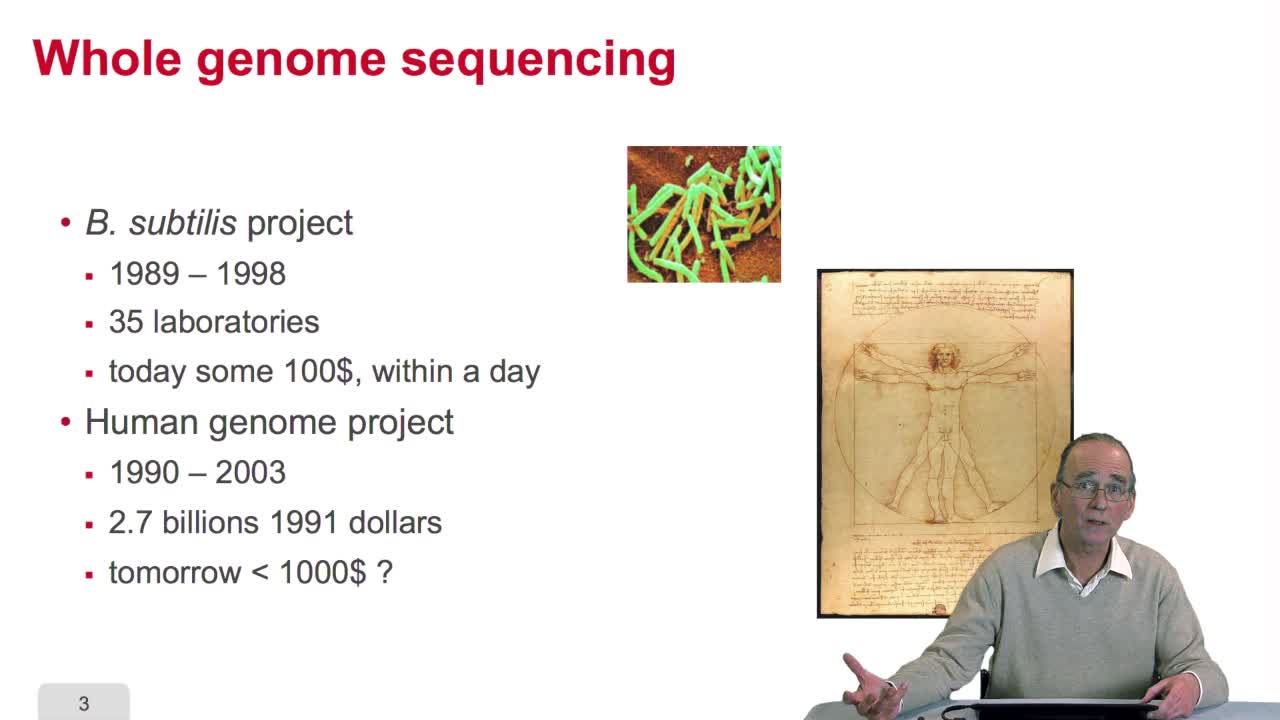
2.9. Whole genome sequencing
RECHENMANN François
Sequencing is anexponential technology. The progresses in this technologyallow now to a sequence whole genome, complete genome. What does it mean? Well let'stake two examples: some twenty years ago,
-
3.7. Index and suffix trees
RECHENMANN François
We have seen with the Boyer-Moore algorithm how we can increase the efficiency of spin searching through the pre-processing of the pattern to be searched. Now we will see that an alternative way of
-
4.4. Aligning sequences is an optimization problem
RECHENMANN François
We have seen a nice and a quitesimple solution for measuring the similarity between two sequences. It relied on the so-called hammingdistance that is counting the number of differencesbetween two
-
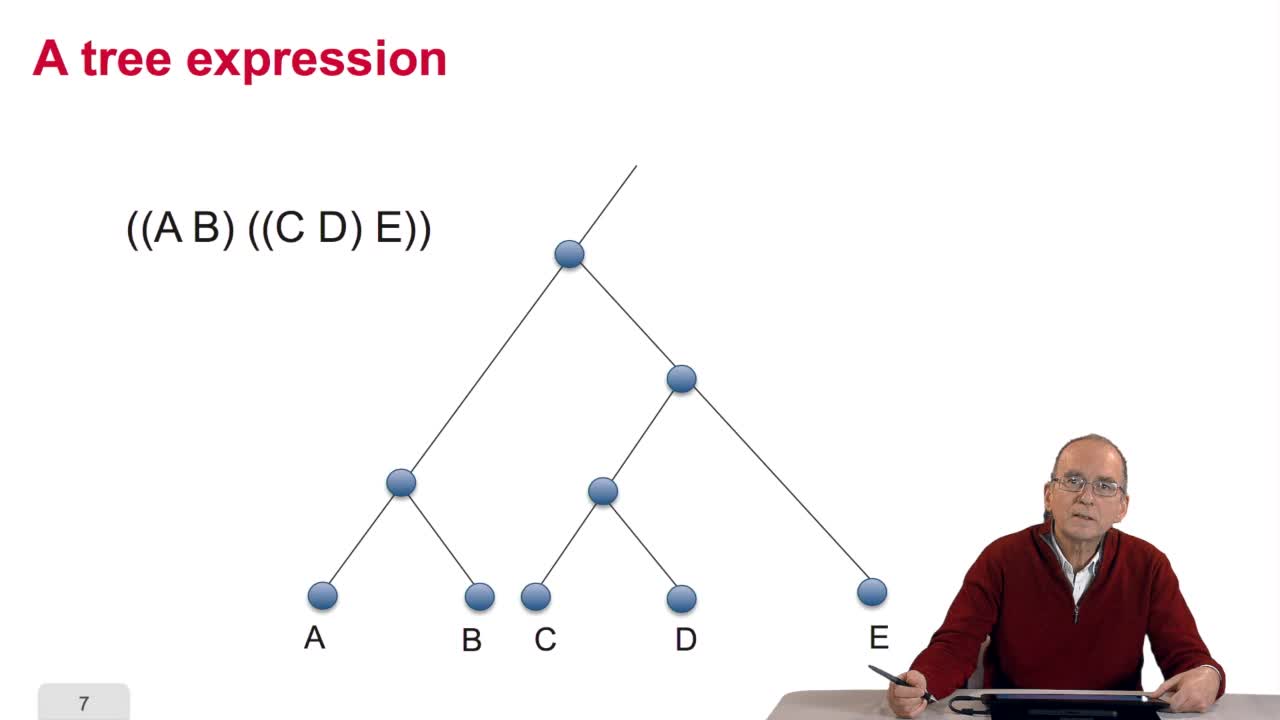
5.2. The tree, an abstract object
RECHENMANN François
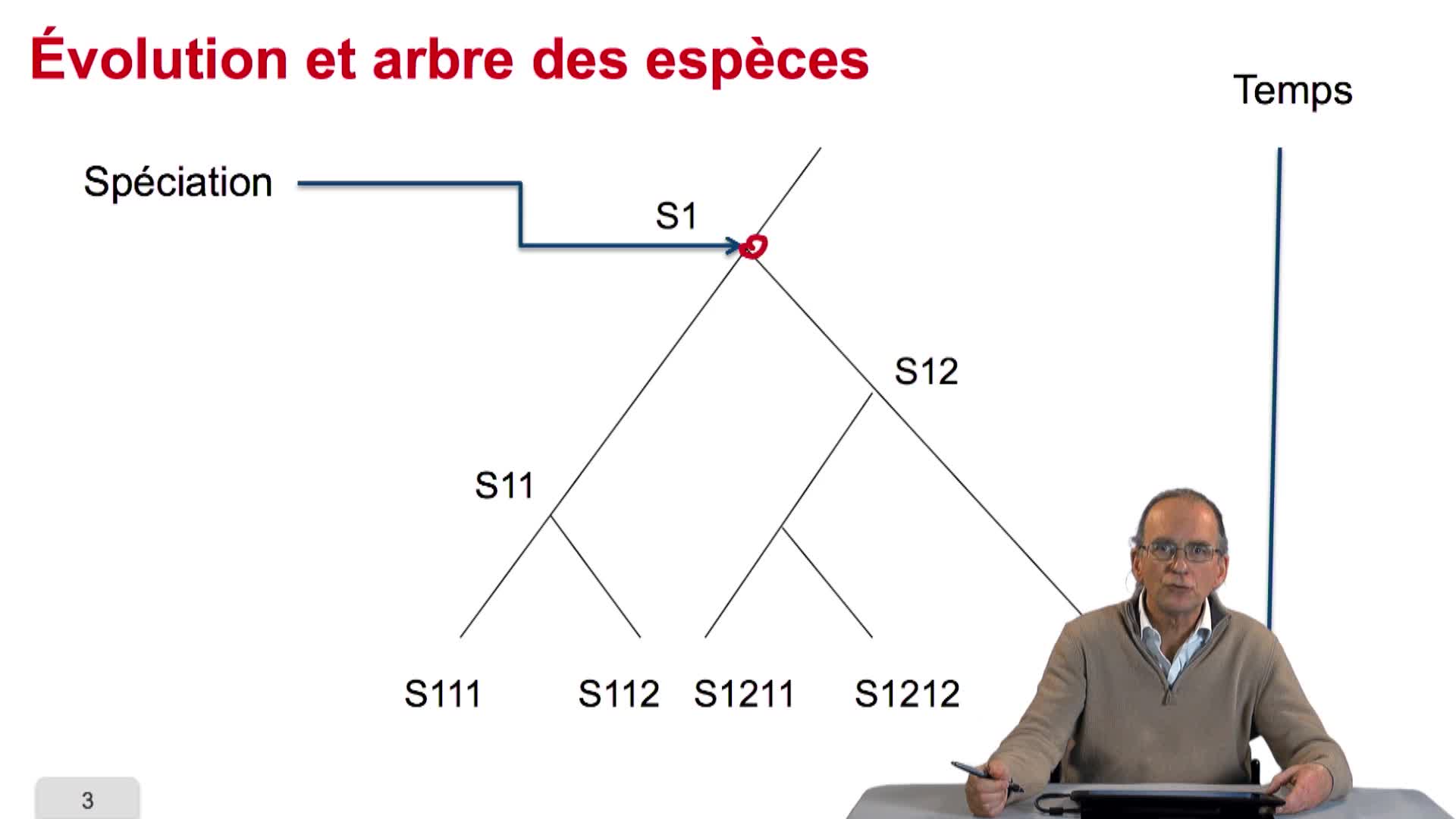
When we speak of trees, of species,of phylogenetic trees, of course, it's a metaphoric view of a real tree. Our trees are abstract objects. Here is a tree and the different components of this tree.
-
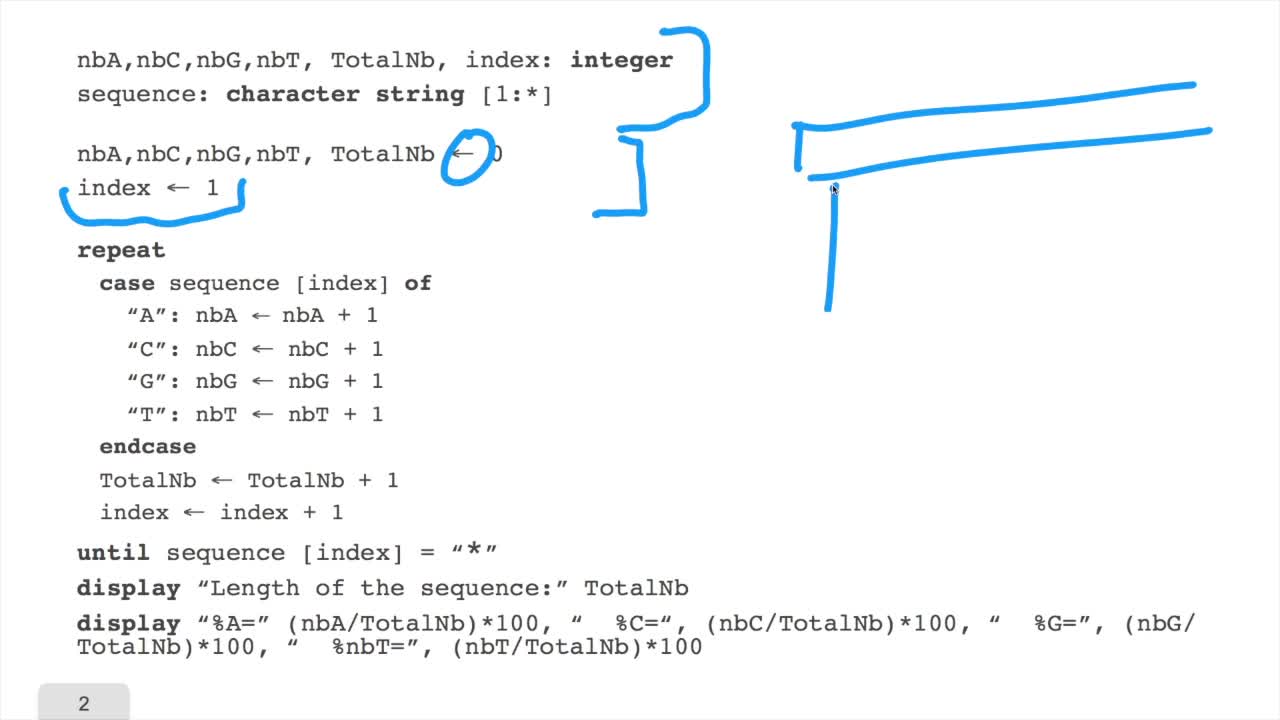
1.6. GC and AT contents of DNA sequence
RECHENMANN François
We have designed our first algorithmfor counting nucleotides. Remember, what we have writtenin pseudo code is first declaration of variables. We have several integer variables that are variables which
Sur le même thème
-
Le projet dnarXiv : Stockage de données sur des molécules d'ADN
LAVENIER Dominique
DUPRAZ Elsa
LEBLANC Julien
COATRIEUX Gouenou
Dominique Lavenier, Elsa Dupraz, Julien Leblanc et Gouenou Coatrieux nous présentent le projet dnarXiv, un projet porté par le LabEx CominLabs qui explore le stockage de données sur des molécules d
-
21 Molecular Algorithms Using Reprogrammable DNA Self-Assembly
WOODS Damien
The history of computing tells us that computers can be made of almost anything: silicon, gears and levers, neurons, flowing water, interacting particles or even light. Although lithographically
-
Des métiers de la bio-informatique
Courtes vidéos pour sensibiliser le jeune public aux débouchés/métiers de la filière numérique et pour promouvoir les sciences du numérique, plus globalement les carrières scientifiques.L'objectif est
-
Reasoning over large-scale biological systems with heterogeneous and incomplete data
SIEGEL Anne
Data produced by the domain of life sciences in the next decade are expected to be highly challenging. In addition to scalability issues which are shared with other applications domains, data produced
-
Biological Networks Entropies: examples in neural, genetic and social networks
DEMONGEOT Jacques
The networks used in biological applications at different scales (molecular, cellular and populational) are of different types, genetic, neuronal, and social, but they share the same dynamical
-
Génomique et informatique
RISLER Jean-Loup
La presse généraliste, et bien entendu la presse spécialisée, se font régulièrement l'écho du séquençage complet d'un nouveau génome. Il est cependant impossible pour le grand public de se rendre
-
Apport de l'informatique à la génomique des cancers
VIARI Alain
La plupart des gènes de notre génome sont présents en deux copies (une sur chaque chromosome homologue). Dans un génome tumoral, en revanche, il est fréquent d'observer soit des pertes soit, au
-
1.4. Qu’est-ce qu’un algorithme ?
RECHENMANN François
PARMENTELAT Thierry
Les génomes peuvent donc être vus comme une longue suite de lettres écrites dans l'alphabet : A, C, G et T. Comment interpréter ces textes ? Ça va être le sujet de la bio-informatique à l'aide d
-
2.2. Les gènes, de Mendel à la biologie moléculaire
RECHENMANN François
PARMENTELAT Thierry
La séquence de caractères est un bon modèle de l'ADN, un des modèles possibles de l'ADN et il est bon parce qu'il est utile. On va voir en particulier que ce modèle simple peut servir de support à de
-
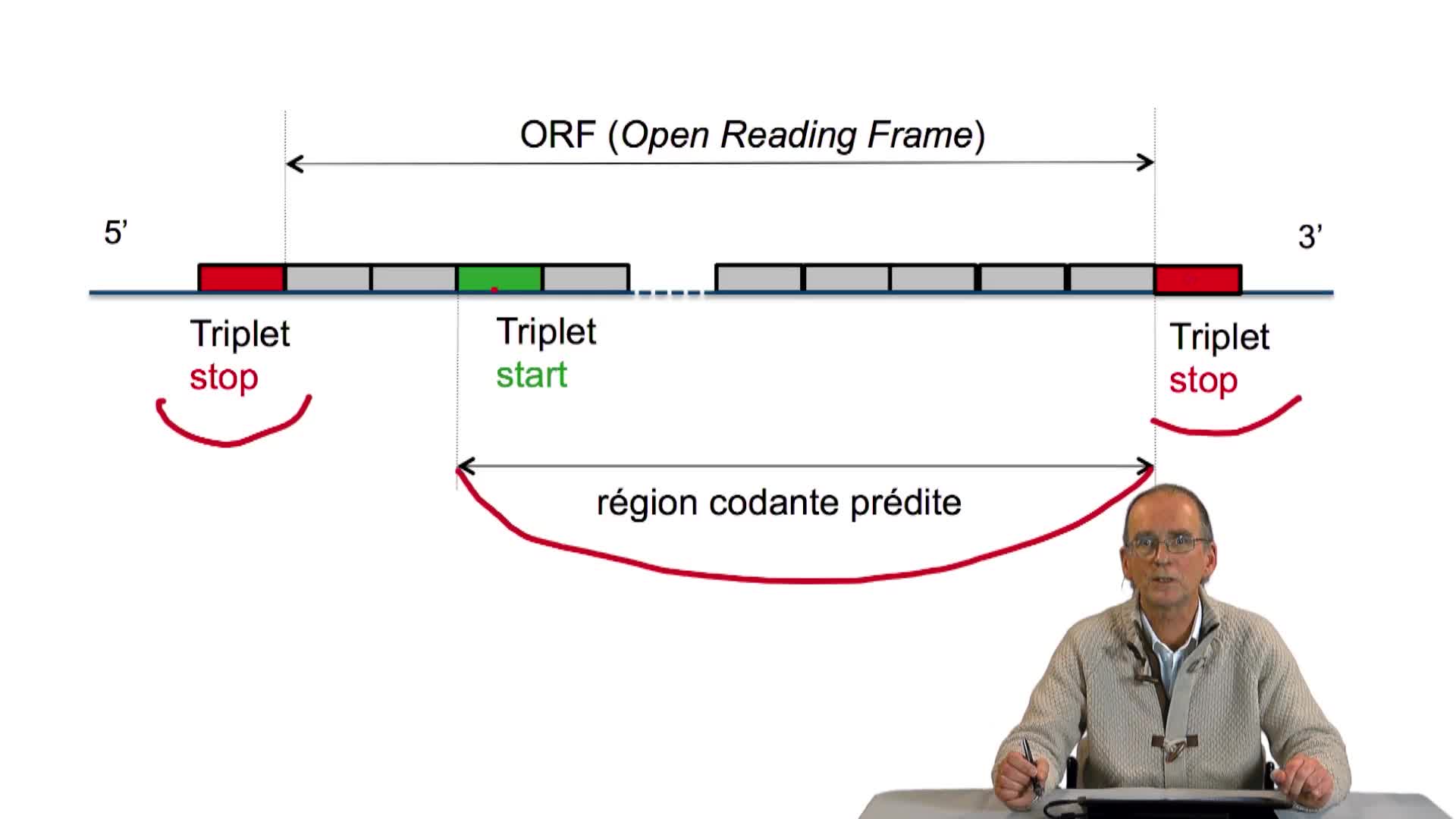
3.1. Tous les gènes se terminent sur un codon stop
RECHENMANN François
PARMENTELAT Thierry
Une fois la séquence d'un génome complet obtenue, débute la phase d'annotation. L'annotation elle-même consiste tout d'abord à rechercher la localisation, c'est-à-dire la position des gènes sur cette
-
3.2. Un algorithme simple de prédiction de gènes
RECHENMANN François
PARMENTELAT Thierry
Sur la base des principes énoncés précédemment, nous allons écrire un premier algorithme de prédiction de gènes sur un texte génomique procaryote. Je rappelle ces principes. L'idée est la suivante :
-
4.2. Évolution et similarité de séquences
RECHENMANN François
PARMENTELAT Thierry
Avant de chercher à quantifier ce qu'est la similarité de séquence, on peut se poser la question même de savoir pourquoi des séquences de génome sont similaires entre organismes. La réponse tient dans