Notice
2.6. Algorithmes + structures de données = programmes
- document 1 document 2 document 3
- niveau 1 niveau 2 niveau 3
Descriptif
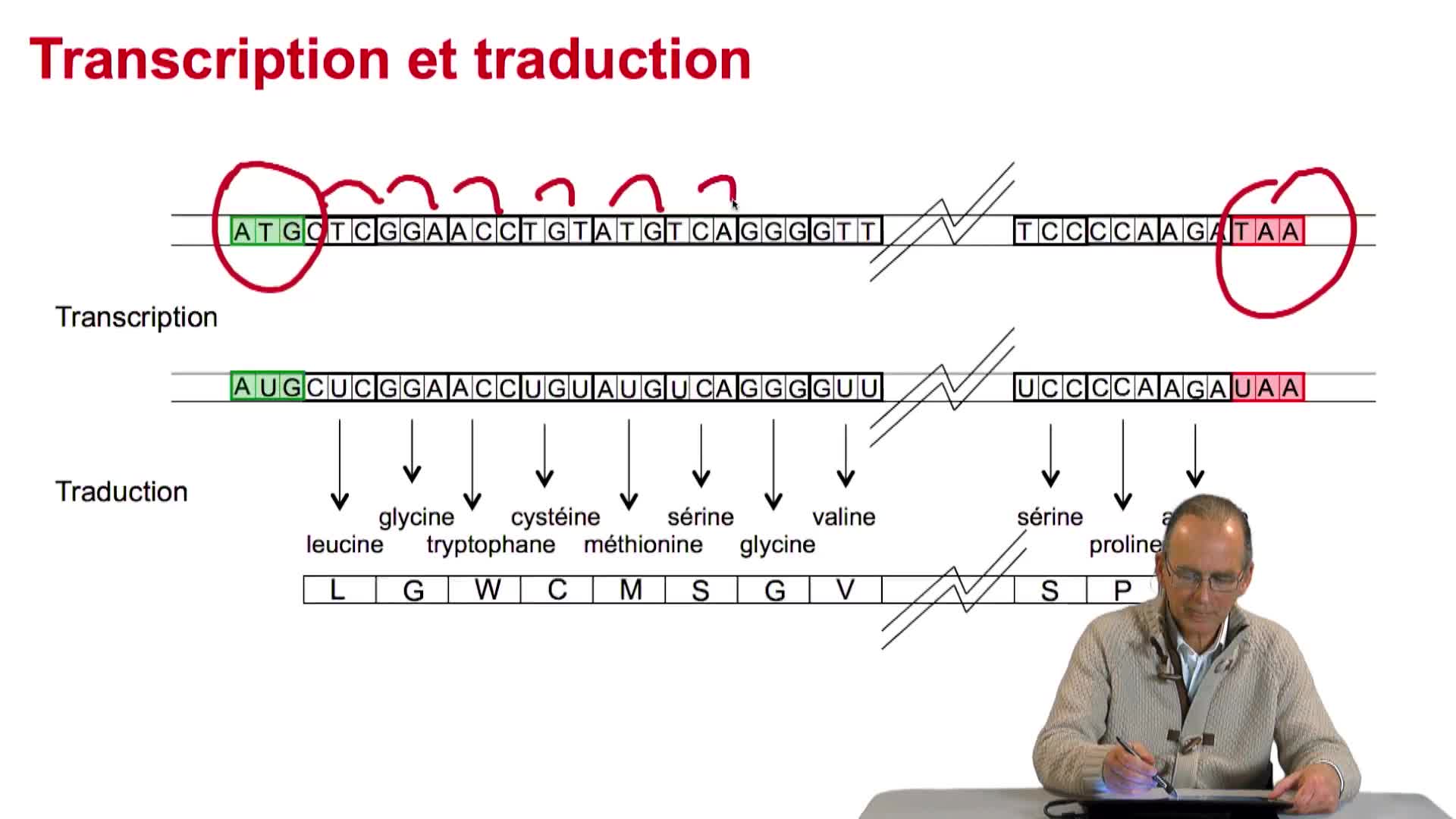
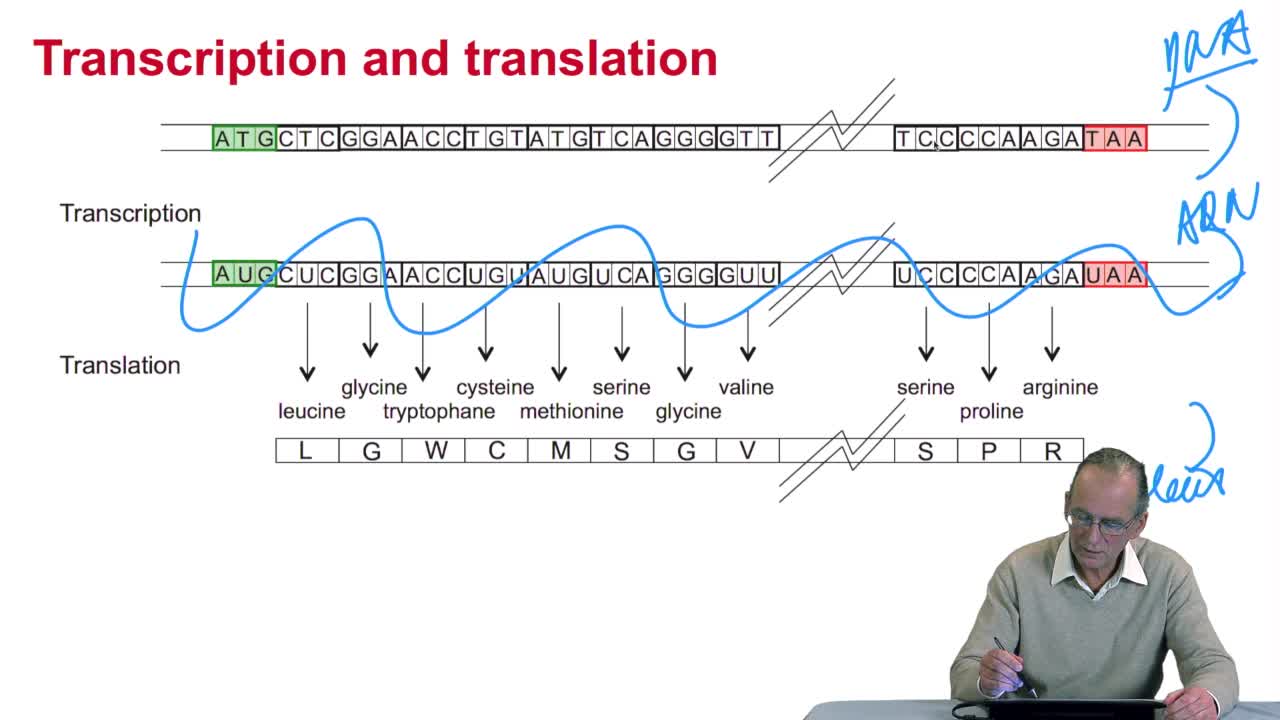
En écrivant le code de la fonction, qui recherche un triplet dans le tableau qui implémente le code génétique, nous avons terminé et obtenu un algorithme de traduction d'une séquence d'ADN, voire d'ARN, en protéines. Arrêtons-nous quelques instants pour évaluer la qualité de cet algorithme, et en particulier ses performances.
Cet algorithme termine-t-il ? Oui. Est-il pertinent ? Oui, dans le sens qu'il effectue effectivement ce qu'on attend de lui, à savoir prendre une séquence dans un alphabet de 4 lettres, grouper chacune de ces lettres 3 par 3, rechercher pour chaque triplet dans le code génétique, plus exactement dans le tableau qui représente le code génétique, l'acide aminé correspondant et rajouter cet acide aminé au bout de la séquence qui représente la protéine en cours de construction. La dernière question, c'est : est-il efficace ? Efficace en temps dans un premier temps...
Intervention / Responsable scientifique
Dans la même collection
-
2.4. Un algorithme de traduction
RechenmannFrançoisParmentelatThierryUne protéine, en tant que succession d'acides aminés, peut-être vue comme le résultat d'un processus de traduction d'une chaîne de caractères écrite dans un alphabet de 4 lettres en une autre chaîne
-
2.8. Les technologies de séquençage de l’ADN
RechenmannFrançoisParmentelatThierryNous parlons beaucoup dans ce cours de séquences génomiques ou séquences d'ADN, que nous voyons pour des raisons algorithmiques sous forme de chaînes de caractères. Comment ces séquences, ces chaînes
-
2.2. Les gènes, de Mendel à la biologie moléculaire
RechenmannFrançoisParmentelatThierryLa séquence de caractères est un bon modèle de l'ADN, un des modèles possibles de l'ADN et il est bon parce qu'il est utile. On va voir en particulier que ce modèle simple peut servir de support à de
-
2.5. Implémenter le code génétique
RechenmannFrançoisParmentelatThierryNous avons écrit le corps de l'algorithme de traduction, et nous avons fractionné la complexité d'écriture de cet algorithme en faisant appel à une fonction qui recherche dans le tableau, qui
-
2.9. Le séquençage de génomes complets
RechenmannFrançoisParmentelatThierryLes progrès dans les technologies de séquençage ont permis d'aborder le séquençage complet de génome. Là encore, les progrès ont été spectaculaires. Prenons l'exemple du projet de séquençage de la
-
2.3. Le code génétique
RechenmannFrançoisParmentelatThierryGènes et protéines, mais qu'est-ce qu'une protéine ? Une protéine, c'est également une molécule qui est constituée d'une succession de ce que l'on appelle les acides aminés. C'est donc une chaîne d
-
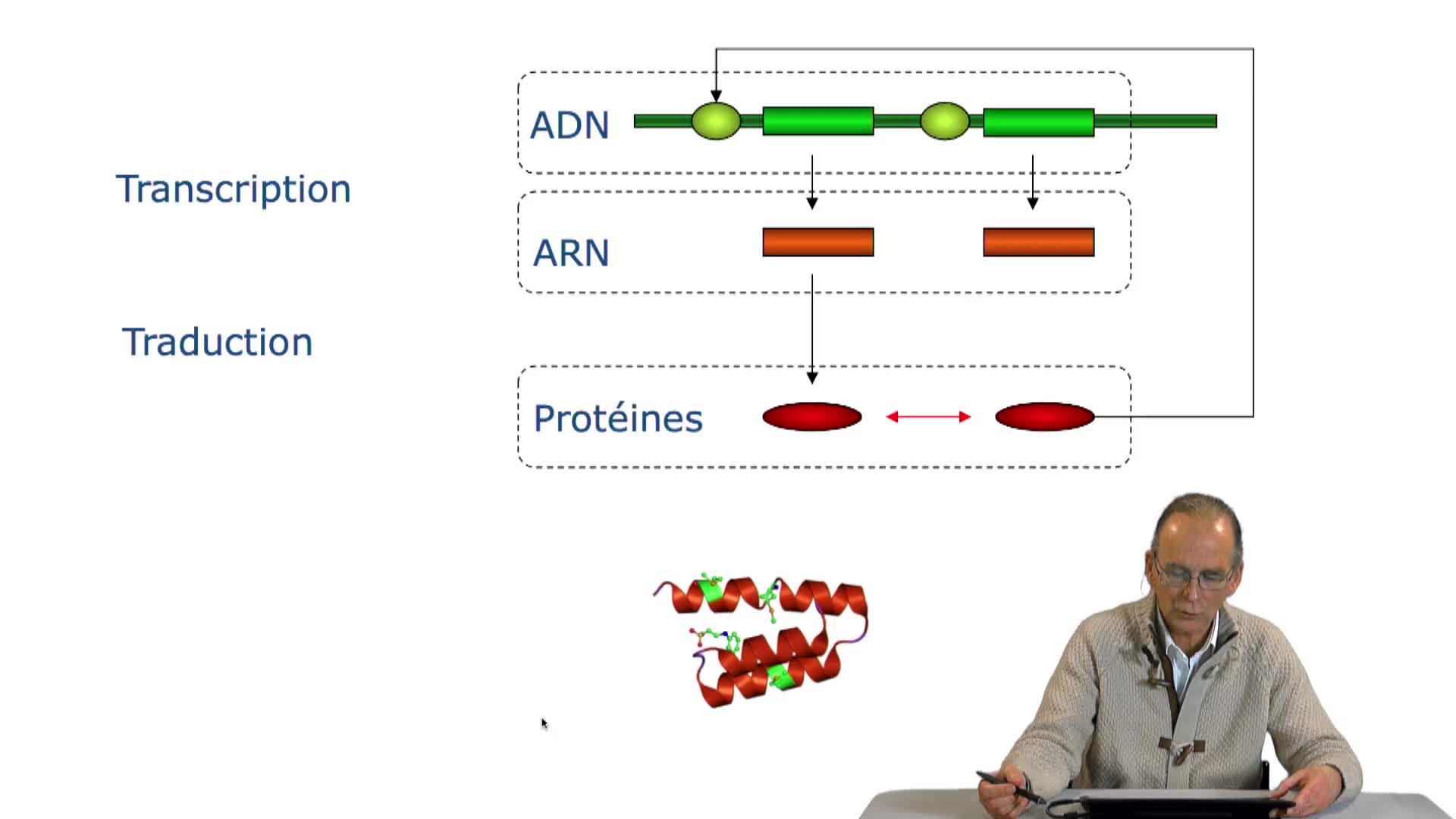
2.7. Les compromis de la conception d’algorithmes
RechenmannFrançoisParmentelatThierryLa mise en oeuvre d'une structure de données appropriée permet, nous l'avons vu, d'améliorer les performances d'algorithmes. Nous en avons vu l'exemple sur la recherche d'un triplet dans un tableau de
-
2.1. La séquence est-elle un bon modèle de l’ADN ?
RechenmannFrançoisParmentelatThierryL'ADN porte l'information génétique, plus précisément l'ADN porte les gènes, c'est-à-dire les régions de cette molécule qui portent l'information utilisée par la cellule pour synthétiser les protéines
-
2.10. Comment trouver les gènes ?
RechenmannFrançoisParmentelatThierryL'obtention de la séquence complète d'un génome d'un organisme vivant est certes un beau résultat, mais c'est en fait le début d'une longue phase d'interprétation, d'annotations et de comparaisons.
Avec les mêmes intervenants et intervenantes
-
1.2. At the heart of the cell: the DNA macromolecule
RechenmannFrançoisDuring the last session, we saw how at the heart of the cell there's DNA in the nucleus, sometimes of cells, or directly in the cytoplasm of the bacteria. The DNA is what we call a macromolecule, that
-
1.10. Overlapping sliding window
RechenmannFrançoisWe have made some drawings along a genomic sequence. And we have seen that although the algorithm is quite simple, even if some points of the algorithmare bit trickier than the others, we were able to
-
2.3. The genetic code
RechenmannFrançoisGenes code for proteins. What is the correspondence betweenthe genes, DNA sequences, and the structure of proteins? The correspondence isthe genetic code. Proteins have indeedsequences of amino acids.
-
3.6. Boyer-Moore algorithm
RechenmannFrançoisWe have seen how we can make gene predictions more reliable through searching for all the patterns,all the occurrences of patterns. We have seen, for example, howif we locate the RBS, Ribosome
-
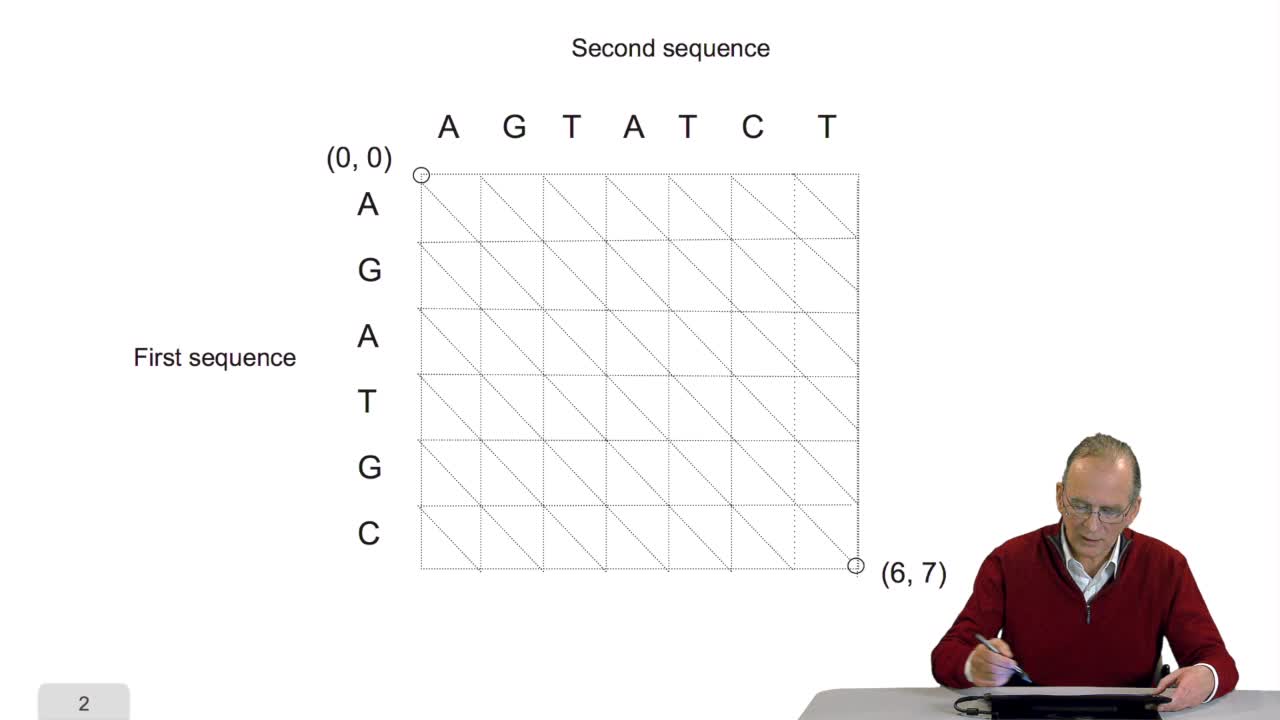
4.5. A sequence alignment as a path
RechenmannFrançoisComparing two sequences and thenmeasuring their similarities is an optimization problem. Why? Because we have seen thatwe have to take into account substitution and deletion. During the alignment, the
-
5.5. Differences are not always what they look like
RechenmannFrançoisThe algorithm we have presented works on an array of distance between sequences. These distances are evaluated on the basis of differences between the sequences. The problem is that behind the
-
1.5. Counting nucleotides
RechenmannFrançoisIn this session, don't panic. We will design our first algorithm. This algorithm is forcounting nucleotides. The idea here is that as an input,you have a sequence of nucleotides, of bases, of letters,
-
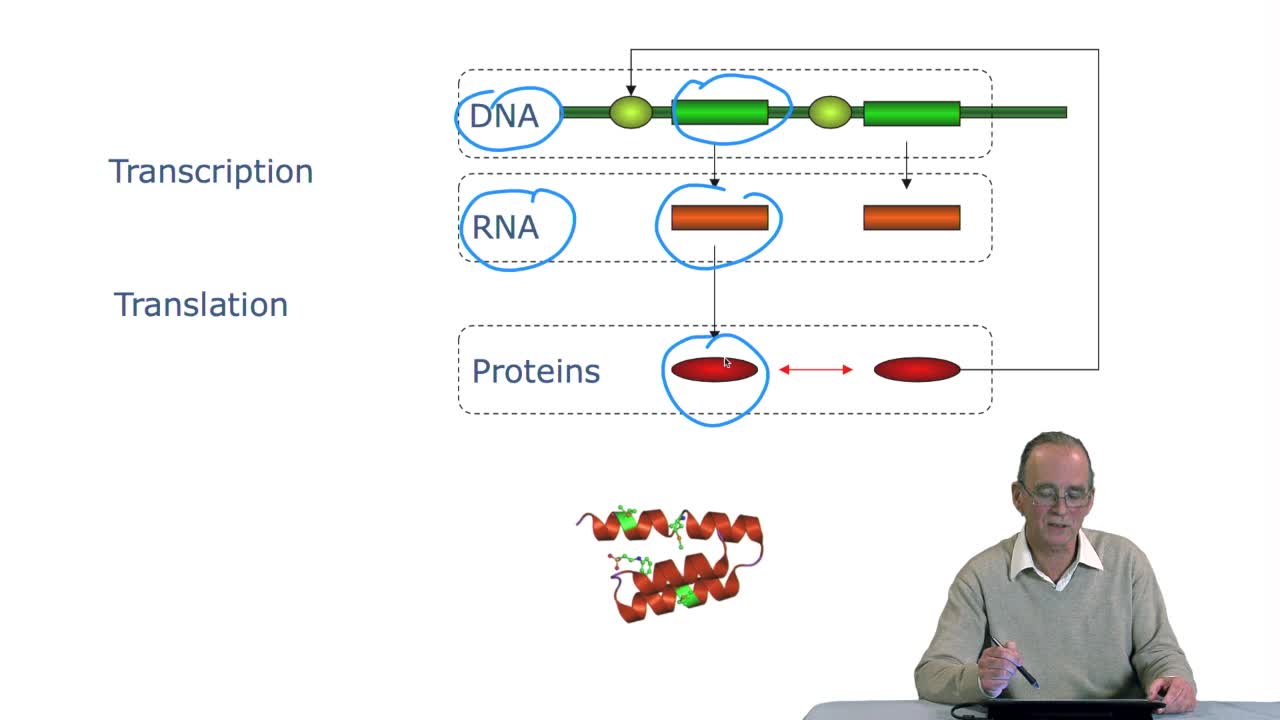
2.4. A translation algorithm
RechenmannFrançoisWe have seen that the genetic codeis a correspondence between the DNA or RNA sequences and aminoacid sequences that is proteins. Our aim here is to design atranslation algorithm, we make the
-
3.1. All genes end on a stop codon
RechenmannFrançoisLast week we studied genes and proteins and so how genes, portions of DNA, are translated into proteins. We also saw the very fast evolutionof the sequencing technology which allows for producing
-
3.9. Benchmarking the prediction methods
RechenmannFrançoisIt is necessary to underline that gene predictors produce predictions. Predictions mean that you have no guarantees that the coding sequences, the coding regions,the genes you get when applying your
-
4.2. Why gene/protein sequences may be similar?
RechenmannFrançoisBefore measuring the similaritybetween the sequences, it's interesting to answer the question: why gene or protein sequences may be similar? It is indeed veryinteresting because the answer is related
-
5.4. The UPGMA algorithm
RechenmannFrançoisWe know how to fill an array with the values of the distances between sequences, pairs of sequences which are available in the file. This array of distances will be the input of our algorithm for
Sur le même thème
-
La voix, une donnée identifiante à protéger
VincentEmmanuelEmmanuel Vincent, chercheur au Centre Inria de l'Université de Lorraine et au Loria (Laboratoire lorrain de recherche en informatique et ses applications), présente sa recherche sur l'anonymisation de
-
Podcast 1/4 d'heure avec : Emmanuel Vincent, chercheur au Centre Inria de l'Université de Lorraine …
VincentEmmanuelRencontre avec Emmanuel Vincent - chercheur au Centre Inria de l'Université de Lorraine et Loria (Laboratoire lorrain de recherche en informatique et ses applications).
-
Stockage de données numériques sur ADN synthétique : Introduction au domaine
AntoniniMarcDuprazElsaLavenierDominiquePrésentation globale des différentes étapes du stockage de données sur des molécules d'ADN synthétique
-
Stockage de données numériques sur ADN synthétique : Production des données: synthèse, séquençage
LavenierDominiqueBarbryPascalDescription des opérations d'écriture et de lecture des molécules d'ADN : synthèse et séquençage.
-
Stockage de données numériques sur ADN synthétique : Reconstruction des données
LavenierDominiqueTraitement des données après séquençage
-
Stockage de données numériques sur ADN synthétique : Codage Canal
DuprazElsaTechniques de codage pour le stockage de données sur ADN
-
Stockage de données numériques sur ADN synthétique : Codage Source
AntoniniMarcCodage source pour le stockage de données sur ADN synthétique
-
Stockage de données numériques sur ADN synthétique : Théorie de l'information
Kas HannaSergeQuelle quantité d'information peut-on stocker et récupérer de manière fiable dans l'ADN ?
-
The tree of life
AbbySophieLes Rencontres Exobiologiques pour Doctorants (RED) sont une école de formation sur les « bases de l'astrobiologie ». L’édition 2025 s’est tenue du 16 au 21 mars au Parc Ornithologique du Teich.
-
Machines algorithmiques, mythes et réalités
MazenodVincentVincent Mazenod, informaticien, partage le fruit de ses réflexions sur l'évolution des outils numériques, en lien avec les problématiques de souveraineté, de sécurité et de vie privée...
-
Désassemblons le numérique - #Episode11 : Les algorithmes façonnent-ils notre société ?
SchwartzArnaudLima PillaLaércioEstériePierreSalletFrédéricFerbosAudeRoumanosRayyaChraibi KadoudIkramUn an après le tout premier hackathon sur les méthodologies d'enquêtes journalistiques sur les algorithmes, ce nouvel épisode part à la rencontre de différents points de vue sur les algorithmes.
-
Les machines à enseigner. Du livre à l'IA...
BruillardÉricQue peut-on, que doit-on déléguer à des machines ? C'est l'une des questions explorées par Éric Bruillard qui, du livre aux IA génératives, expose l'évolution des machines à enseigner...